Cientistas acabam de descobrir o “interruptor principal” para o crescimento das plantas.
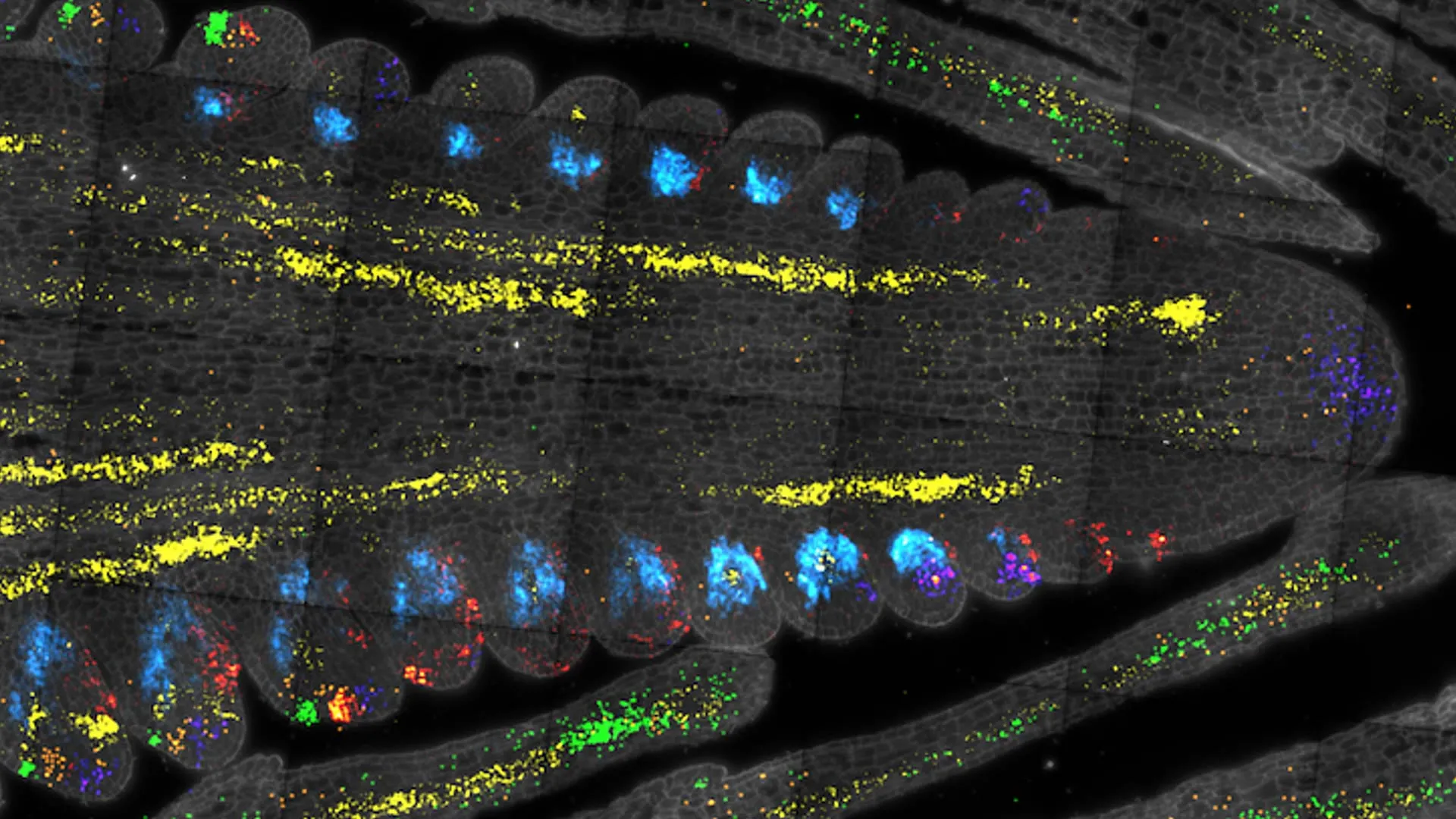
As células-tronco vegetais são essenciais para o abastecimento alimentar global, a alimentação animal e a produção de combustíveis. Elas formam a base do crescimento das plantas. No entanto, muitos aspectos sobre esses componentes enigmáticos ainda são obscuros. Análises anteriores não conseguiram identificar vários dos genes fundamentais que regulam o funcionamento dessas células.
Agora, pela primeira vez, biólogos de plantas do Cold Spring Harbor Laboratory (CSHL) mapeiam dois reguladores de células-tronco conhecidos em milhares de células de brotos de milho e Arabidopsis. A pesquisa também revelou novos reguladores de células-tronco em ambas as espécies e relacionou alguns a variações de tamanho no milho. Este método para recuperar células-tronco raras pode ser aplicado por todo o reino vegetal. O professor David Jackson, do CSHL, afirma: “Idealmene, gostaríamos de descobrir como formar uma célula-tronco. Isso nos permitiria regenerar plantas de maneira mais eficaz e compreender a diversidade vegetal. Um aspecto que entusiasma as pessoas é o desenvolvimento de novas culturas que sejam mais resistentes ou produtivas. Ainda não temos uma lista completa de reguladores—os genes que precisamos para isso.”
Jackson e sua equipe inicialmente concentraram-se em dois reguladores de células-tronco bem conhecidos chamados CLAVATA3 e WUSCHEL. Um ex-pós-doutorando no laboratório de Jackson, Xiaosa Xu, cuidadosamente dissecou um pequeno pedaço de brotos de milho e Arabidopsis que continham células-tronco. Em seguida, a equipe utilizou uma máquina de “microfluídica” para separar cada célula, converter seu RNA em DNA e rotulá-la com uma identificação que indica de qual célula foi originada.
O processo, conhecido como sequenciamento de RNA em célula única, permite que os pesquisadores analisem a expressão gênica em milhares de células simultaneamente. “A grande vantagem é que temos este atlas de expressão gênica,” afirma Jackson. “Quando publicarmos isso, toda a comunidade poderá utilizar. Outras pessoas interessadas em células-tronco de milho ou Arabidopsis não precisarão repetir o experimento. Elas poderão utilizar nossos dados.”
O sequenciamento de RNA em célula única permitiu à equipe recuperar cerca de 5.000 células expressando CLAVATA3 e 1.000 células expressando WUSCHEL. A seguir, identificaram centenas de genes que eram expressos preferencialmente em células-tronco de milho e Arabidopsis, sugerindo que podem ter importância evolutiva em diversas espécies vegetais. A partir daí, puderam associar certos reguladores de células-tronco à produtividade no milho. Essas associações poderão um dia ajudar os criadores a selecionar linhagens específicas para produção de alimentos, ração animal ou combustíveis.
“É um conhecimento fundamental que pode orientar a pesquisa na próxima década,” comenta Jackson. “Isso pode ser utilizado não apenas por biólogos do desenvolvimento, mas também por fisiologistas, que refletem sobre como as espigas de milho crescem e como melhorar a produtividade, e então pelos plantadores.”
Últimas postagens
Você Também Pode Gostar

Todas as manchetes e destaques do dia do radiocMadeira.pt, entregues diretamente para você. Change the color of the background to the green indicated previously and make it occupy all the screen widely.
PRINCIPAIS NOTÍCIAS
© 2025 radiocmadeira. Todos os direitos reservados